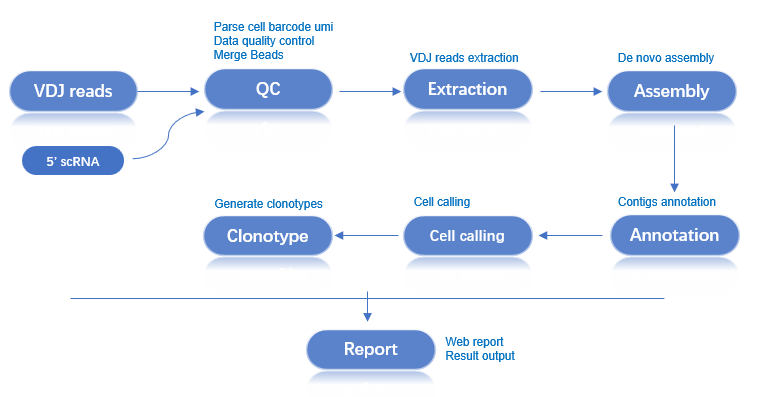
本文档详细介绍了使用 dnbc4tools 进行单细胞 VDJ 测序数据分析的完整流程。
工作流程:5端转录组分析 → VDJ文库处理 → 序列组装注释 → 细胞过滤 → 克隆型分析 → 分析报告

转录组分析请参考 dnbc4tools rna run。5'端转录组分析主流程需在单细胞RNA主流程分析基础上添加参数 --end5。
为单个样本生成表达矩阵,以下是一个示例步骤或脚本模板:
$dnbc4tools rna run \
--name sample_5rna \
--cDNAfastq1 /data/sample_cDNA_R1.fastq.gz \
--cDNAfastq2 /data/sample_cDNA_R2.fastq.gz \
--oligofastq1 /data/sample_oligo1_1.fq.gz,/data/sample_oligo2_1.fq.gz \
--oligofastq2 /data/sample_oligo1_2.fq.gz,/data/sample_oligo2_2.fq.gz \
--genomeDir /opt/database/Homo_sapiens \
--threads 30 \
--end5
分析需要以下文件:
| 文件类型 | 说明 |
|---|---|
| FASTQ文件 | VDJ文库测序数据,包含TCR或BCR序列信息 |
| singlecell.csv文件 | 5端转录组分析结果中的细胞信息文件 |
分析需要5'端转录组分析结果目录中的 singlecell.csv 文件。该文件包含 cell 和 barcode 列的合并信息,以及 is_cell_barcode 列(1表示细胞,0表示非细胞),用于鉴定有效的细胞。
参考示例文件内容:
cell,reads,gene,umi,is_cell_barcode,barcode
CELL1118_N3,1485813,5693,57580,1,AGATCGCCTACGATCACGAT;GGTGGAAGGTGAGAGAAGCG;GTAGTTCTAGGCTAAGTACT
CELL1651_N3,805447,4881,32131,1,ATCTCAAGCCCACCGTGTGT;CATCAATTAAGTGATCGCAT;CCTAACTGAGGAACGCTTAG
CELL4_N3,820269,5649,30326,1,AACACCTGATCGTTCAATAA;AATTCGAAGGTAGTCGGAAT;CACATGTTACATGTTCTATA
CELL906_N3,656624,4853,28142,1,ACGTCCGCGTGACCATGTGC;AGGAGCTCCATTGATCTTAA;CAATCCGGAGAACGTATCTG
CELL1577_N2,672637,4610,24822,1,ATATTCTCACGTAACGGATG;TAGGAACTCGGCTTAGATCT
CELL2064_N2,542608,2355,23324,1,CATAAGCACTCACCGCTAGT;GTCTCACAGTTGTTCACTAG
CELL1332_N6,580950,4702,22953,1,AGGTGTAAGCCTACCGGACC;CGCACTCACCTAACATTGTG;CTTGCCGCGCTATCAATGCA;GCCACTAGTCGACGCGGTTG;GTCAGCATGCTCTTCCACAG;TCGATATCCTCACTCTTAAC
CELL726_N4,585934,4617,22660,1,ACCTACGGCGTTACTATGTG;CGACGCTCTCGACAGTTAGG;CGGCAGAGTCTTGGCGCTTA;TCCGACCGTATCTTCATCTC
CELL4010_N1,555308,4268,22554,1,AGAGAGTCGCAGCAAGCGAC
VDJ主分析流程结合了单细胞VDJ文库测序数据和对应样本的5'转录组分析结果,包含以下关键步骤:
为单个样本运行TCR分析,以下是一个示例步骤或脚本模板:
$dnbc4tools vdj run \
--name sample_tcr \
--fastq1 /data/sample_tcr_R1.fastq.gz \
--fastq2 /data/sample_tcr_R2.fastq.gz \
--ref human \
--chain TR \
--beadstrans /sample_5rna/outs/singlecell.csv \
--threads 10
为单个样本运行BCR分析,以下是一个示例步骤或脚本模板:
$dnbc4tools vdj run \
--name sample_bcr \
--fastq1 /data/sample_bcr_R1.fastq.gz \
--fastq2 /data/sample_bcr_R2.fastq.gz \
--ref human \
--chain IG \
--beadstrans /sample_5rna/outs/singlecell.csv \
--threads 10
在对暗反应自动检测后,软件开始运行分析,以下是一个示例:
2025-04-23 23:01:01 Performing VDJ data processing
Chemistry(darkreaction) determined in fastqR1: darkreaction
2025-04-23 23:01:02 Processing VDJ library filtering...
...done
2025-04-23 23:31:13 Preparing data for VDJ assembly...
...done
2025-04-24 00:21:14 Sequence Assembly and annotation of VDJ Gene Segments
...done
2025-04-24 02:49:16 Cell calling for VDJ analysis...
...done
2025-04-24 02:51:52 Generating VDJ clonotype analysis...
...done
2025-04-24 02:53:49 Converting VDJ results from cellbarcode to cellid...
...done
2025-04-24 02:53:58 Statistical analysis and report generation for results.
...done
Analysis Finished Elapsed Time: 3:53:07
成功的运行会以 Analysis Finished 结束。
分析完成后,将生成结果输出目录outs,logs日志目录,其中outs目录包括:
.
├── airr_annotations.tsv
├── all_contig_annotations.csv
├── all_contig.fasta
├── all_contig.fasta.fai
├── *_scVDJ_IG_report.html
├── clonotypes.csv
├── consensus_annotations.csv
├── consensus.fasta
├── consensus.fasta.fai
├── filtered_contig_annotations.csv
├── filtered_contig.fasta
├── filtered_contig.fasta.fai
└── metrics_summary.xls
相关文档:
内容待补充